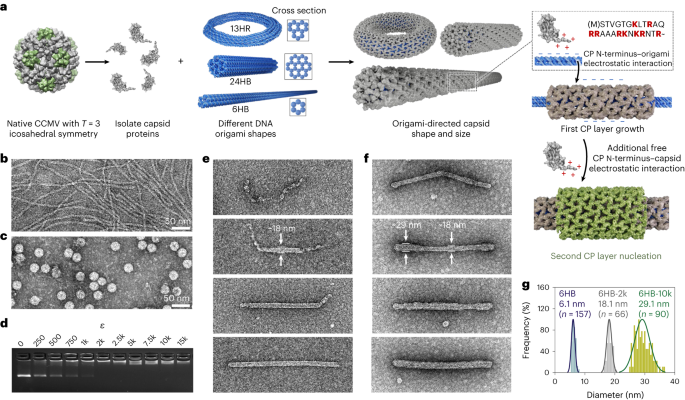
Gấp và tinh lọc DNA origami
Các cấu trúc origami DNA (6HB, 24HB, 60HB, 13HR và nanocapsule) được gấp lại trong phản ứng một bình bằng cách giảm dần nhiệt độ bằng hệ thống PCR Proflex 3 × 32 giếng (Thermo Fisher). Các chuỗi giàn giáo (các biến thể p7249, p8064 và p7560 của M13mp18 chuỗi đơn) được mua từ Tilibit Nanosystems và các chuỗi chủ yếu từ Công nghệ DNA tích hợp. Để đảm bảo năng suất gấp DNA origami cao, các điều kiện tối ưu hóa dành riêng cho cấu trúc liên quan đến cả quy trình ủ và lựa chọn bộ đệm ('bộ đệm gấp', FOB) được sử dụng (Ghi chú bổ sung 20).
Trao đổi bộ đệm cho DNA origami
Các cấu trúc origami DNA tinh khiết được chuyển vào dung dịch đệm 6.5, 4 mM 2-(1-hydroxyethyl) -2-piperazine ethanesulfonic acid (HEPES) được bổ sung 6.5 mM NaOH (HEPES-NaOH, pH XNUMX) trước khi tạo phức với CCMV CP. Việc trao đổi bộ đệm được thực hiện bằng phương pháp lọc quay59 sử dụng bộ lọc ly tâm cắt trọng lượng phân tử 100 kDa (MWCO) (Amicon), được rửa sạch trước khi sử dụng bằng cách ly tâm với 400 μl dung dịch đệm HEPES-NaOH trong 5 phút ở mức 14,000g. Sau đó, các thể tích bằng nhau của dung dịch DNA origami và dung dịch đệm HEPES-NaOH được thêm vào thiết bị lọc và quá trình ly tâm được tiếp tục trong 10 phút ở tốc độ 6,000.g. Sau đó, một thể tích HEPES-NaOH bằng 2.09 × thể tích ban đầu của dung dịch origami được thêm vào và bước ly tâm được lặp lại. Mẫu được thu thập bằng cách đảo ngược bộ lọc và ly tâm trong 2.5 phút ở tốc độ 1,000g.
Cách ly CP CCMV
Các CP được phân lập từ CCMV nguyên vẹn (để chuẩn bị vi rút, xem Ghi chú bổ sung 21). Tóm lại, các hạt vi rút được thẩm tách qua đêm trên 50 mM Tris–HCl, 500 mM CaCl2 đệm, pH 7.5 được bổ sung 1 mM dithiothreitol (DTT) bằng cốc lọc máu mini Slize-A-Lyzer (3.5 kDa MWCO, Thermo Scientific). RNA được tạo thành từng viên trong bước ly tâm ở 4°C sử dụng 21,100g trong 6 giờ và chất nổi phía trên thu hồi được thẩm tách qua đêm dựa trên 'dung dịch đệm sạch' chứa 50 mM Tris–HCl, 150 mM NaCl ở pH 7.5 được bổ sung 1 mM DTT (được điều chỉnh từ ref. 60). Nồng độ của protein được xác định dựa trên độ hấp thụ của chúng ở bước sóng 280 nm (hệ số tuyệt chủng, 23,590 M-1 cm-1) bằng Máy quang phổ vi bản BioTek Eon (mẫu 2 μl, tấm Take3).
TUỔI TÁC
AGE được sử dụng để nghiên cứu sự tương tác liên kết giữa protein và cấu trúc origami bằng cách theo dõi sự thay đổi khả năng di chuyển điện di. Hơn nữa, tính nguyên vẹn của cấu trúc origami sau khi gấp và tinh chế, cũng như trong quá trình tiêu hóa DNase I, được phân tích bằng phương pháp điện di trên gel. Để đạt được mục đích này, các mẫu (thể tích từ 10 đến 32 μl) được bổ sung thuốc nhuộm tải gel 6× (40% sucrose không có thuốc nhuộm đối với các mẫu từ nghiên cứu tiêu hóa) được chạy trong gel agarose 2% (w/v) (1 × Tris Dung dịch đệm –acetate–ethylenediaminetetraacetic acid (TAE), 11 mM MgCl2) trong 45 phút ở 90 V trong đệm 1 × TAE bổ sung 11 mM MgCl2. Để nhuộm màu, ethidium bromide (EtBr) ở nồng độ cuối cùng là 0.46 μg ml-1 đã được sử dụng và DNA được hiển thị dưới ánh sáng cực tím bằng hệ thống GelDoc XR+ (Bio-Rad).
Sự tạo phức của DNA origami và CCMV CP
Sự tạo phức giữa CP và DNA origami được thực hiện ở nồng độ origami cuối cùng là 4 nM (mẫu 10 μl). Origami đã được thêm vào dung dịch protein đã được pha loãng trong 'dung dịch đệm sạch' theo tỷ lệ thể tích 1:1. Tùy theo lượng protein dư thừa cần thiết, ε, mô tả tỷ lệ mol giữa CP và origami DNA, các dung dịch protein nằm trong khoảng từ 0 đến 60 μM (tương ứng với ε = 0–15k) đã được chuẩn bị. Nồng độ NaCl được điều chỉnh thành 150 mM, tạo ra dung dịch đệm tạo phức chứa 3.25 mM HEPES-NaOH, 25 mM Tris–HCl, 150 mM NaCl và 0.5 mM DTT. Quá trình tạo phức được thực hiện ở 4°C trong ít nhất 1 giờ và sau đó được phân tích bằng AGE và TEM.
Xét nghiệm tiêu hóa DNase I
Để nghiên cứu tác dụng bảo vệ của lớp phủ CP chống lại sự xuống cấp của cấu trúc origami bởi DNase I, 2 μl DNase I dự trữ (dao động từ 0 đến 500 KU ml-1) đã được thêm vào 16 µl mẫu. Ngoài ra CaCl2 và MgCl2 nồng độ đã được điều chỉnh, dẫn đến thể tích phản ứng cuối cùng là 20 μl chứa 3.2 nM DNA origami, 2.6 mM HEPES-NaOH, 20 mM Tris–HCl, 120 mM NaCl, 0.4 mM DTT, 1 mM CaCl2 và 5mM MgCl2. Các mẫu được ủ ở 37°C trong 15 phút (6HB) và 60 phút (24HB). Trước khi phân tích kết quả bằng AGE, các mẫu được tạo phức với CP đã được tách rời bằng cách sử dụng muối natri heparin làm chất liên kết cạnh tranh (nồng độ cuối cùng là 1.5 μM đối với 6HB-2k và 24HB-2.5k và 82 μM đối với 6HB-10k và 24HB-10k; Phần bổ sung Ghi chú 14).
Gấp và tinh lọc RNA-DNA origami
Đối với origami lai RNA-DNA (RNA-6HB), EGFP mRNA (CleanCap EGFP mRNA, TriLink Bio Technologies, L-7601) đã được sử dụng làm giàn giáo. Trong phản ứng một bình, giàn giáo mRNA dài 996 nt được ủ nhiệt với 29 sợi chủ yếu (được mua từ Công nghệ DNA tích hợp, xem Ghi chú bổ sung 22) thành cấu trúc 6HB ngắn bằng hệ thống PCR Proflex 3 × 32 giếng (Thermo Fisher). Cấu trúc được thiết kế để chứa hai giàn giáo chéo và có bước xoắn 11 bp mỗi vòng. Đối với phản ứng gấp, mRNA và ghim được pha loãng thành 1 × FOB chứa 1 × TAE pH 8.4, 5 mM MgCl2 và 1 mM NaCl đạt nồng độ cuối cùng lần lượt là 50 nM và 500 nM. Hỗn hợp phản ứng được ủ ở 55°C trong 15 phút61 và làm nguội bằng cách đặt trên đá ít nhất 10 phút trước khi bảo quản ở 4°C. Để xác thực việc gấp, bốn sợi ghim được trao đổi bằng các sợi ghim có phần nhô ra 3′ (được dán nhãn F, Bảng bổ trợ 2). Chuỗi đính kèm chứa fluorophore (ATTO590, Công nghệ DNA tích hợp), được thêm vào hỗn hợp gấp với tỷ lệ vượt quá 10× cho mỗi vị trí đính kèm, sau đó có thể được tích hợp vào cấu trúc bằng cách lai với phần nhô ra của ghim.
Các cấu trúc gấp được làm sạch khỏi các sợi ghim dư thừa bằng cách lọc quay. Để đạt được mục đích này, bộ lọc (100 kDa MWCO, Amicon) được rửa bằng 400 μl 1 × FOB bằng cách ly tâm ở tốc độ 14,000g trong 5 phút, sau đó bổ sung hai lần 40 μl RNA-6HB cùng với 40 μl 1 × FOB. Sau bước ly tâm ở tốc độ 6,000g trong 10 phút, 80 µl 1 × FOB được thêm vào và quá trình ly tâm tiếp tục (6,000g, 10 phút). Bước rửa này được lặp lại tổng cộng ba lần trước khi mẫu được thu hồi bằng cách đảo ngược bộ lọc vào ống sạch (1,000g, 2.5 phút). Nồng độ được xác định bằng cách đo độ hấp thụ ở bước sóng 260 nm (hệ số tuyệt chủng, 1.29 × 107 M-1 cm-1) và khả năng gấp thành công được xác định bằng gel AGE (3.5% (w/v), hiển thị dưới ánh sáng cực tím (kênh EtBr) và ánh sáng đỏ (kênh A647), hệ thống ChemiDoc MP, Bio-Rad), AFM và TEM.
Sự tạo phức của CP origami RNA-6HB và CCMV
Để tạo phức, origami RNA-6HB tinh khiết trong 1 × FOB được trộn với các viên nang CCMV trong 'đệm sạch' theo tỷ lệ 1: 1 ở nồng độ origami lai cuối cùng là 7.5, 45 nM. Điều này dẫn đến một dung dịch đệm tạo phức chứa 75.5 mM Tris, 10 mM NaCl, 2.5 mM axit axetic, XNUMX mM MgCl2, 0.5 mM DTT và 0.5 mM EDTA. Các mẫu được ủ ở 4°C trong ít nhất 1 giờ trước khi phân tích bằng AGE và TEM.
Sự phức hợp của DNA origami và NoV CP
NoVLP đã được chuẩn bị theo báo cáo của Lampinen et al.62 và được bảo quản trong dung dịch muối đệm phốt phát 1 × (PBS, 137 mM NaCl, 2.7 mM KCl, 10 mM Na2HPO4 và 1.8 mM KH2PO4, pH 7.4); tuy nhiên, ở đây SpyTag003 (ref. 63) đã được hợp nhất với đầu C của VP1 từ chủng NoV Hu/GII.4/Sydney/NSW0514/2012/AU. Các hạt được kiểm soát chất lượng bằng phương pháp tán xạ ánh sáng động để hình thành hạt, điện di trên gel natri dodecyl sulfate polyacrylamide để xác định độ tinh khiết của protein và đo DSDNA còn lại. Để tạo phức với DNA origami, DNA origami đã có mặt trong mẫu trong cả quá trình tháo gỡ và lắp ráp lại các VLP. Để đạt được mục đích này, các cấu trúc origami được chuyển vào nước khử ion bằng phương pháp lọc quay (như mô tả ở trên). Origami DNA được trộn với NoVLP ở các nồng độ khác nhau theo tỷ lệ 1:4 (v/v), dẫn đến nồng độ origami cuối cùng là 6 nM (mẫu 30 μl). Các mẫu được chuyển vào cốc lọc máu 3.5 kDa MWCO (Slize-A-Lyzer, Thermo Scientific) và được thẩm tách qua đêm ở 4°C so với 50 mM Tris–HCl, pH 8.9. Để lắp ráp lại, ở bước thứ hai, các mẫu được thẩm tách qua đêm ở 4°C với dung dịch đệm natri photphat 100 mM, pH 6.0, tương tự như báo cáo của White et al.64 Sự phức tạp trong quá trình tháo gỡ và lắp ráp NoVLP được phân tích bằng AGE và TEM.
Sự tạo phức của DNA origami và SV40 CP
SV40 chính CP VP1 (abcam, ab74565) đã được tháo rời và lắp ráp lại (điều chỉnh từ ref. 50) bằng cách thẩm tách các VLP đã lắp ráp trong PBS với 20 mM Tris, 2 mM DTT, 5 mM EDTA và 50 mM NaCl, pH 8.9 trong 2 giờ ở 4 ° C (3.5 kDa MWCO, Slize-A-Lyzer, Thermo Scientific), sau trong đó nồng độ EDTA đã giảm bằng một bước lọc máu bổ sung ở 4°C trong 2 giờ so với 20 mM Tris, 2 mM DTT, 2 mM EDTA và 50 mM NaCl, độ pH 8.9. Nồng độ được xác định dựa trên độ hấp thụ ở bước sóng 280 nm (hệ số tắt VP1, 32,890 M-1 cm-1). DNA origami được chuyển vào dung dịch đệm HEPES 100 mM, pH 7.2, được bổ sung 125 mM NaCl bằng cách lọc quay (như mô tả ở trên). Các protein được trộn với DNA origami theo tỷ lệ 1:1 (v/v) để đạt nồng độ cuối cùng lần lượt là 0–20 μM và 2 nM, và các mẫu được ủ trong 24 giờ ở nhiệt độ phòng trước khi phân tích bằng AGE và TEM .
Sự tạo phức của DNA origami và MPyV CP
Để tạo phức các capsomer VP1 (để biểu hiện và tinh chế tái tổ hợp, xem Ghi chú bổ sung 23) và DNA origami, cấu trúc origami lần đầu tiên được chuyển vào dung dịch đệm Tris 40 mM, pH 8.0, được bổ sung axit axetic 20 mM, EDTA 2 mM và MgCl 12 mM2 sử dụng lọc quay (xem ở trên). Tùy thuộc vào lượng protein dư thừa mong muốn, ε, capsomer được pha loãng thành 'dung dịch đệm lưu trữ', chứa 40 mM Tris, 200 mM NaCl, 1 mM EDTA, 5% (v/v) glycerol và 5 mM DTT, độ pH 8.0. Để tạo phức, các capsome VP1 được pha loãng theo tỷ lệ 1:20 trong dung dịch origami, dẫn đến nồng độ origami cuối cùng là 0.75 nM (30 μl mẫu) và dung dịch đệm tạo phức chứa 40 mM Tris, 19 mM axit axetic, 1.95 mM EDTA, 11.4 mM MgCl2, 10 mM NaCl, 0.25% (v/v) glycerol và 0.25 mM DTT, pH 8. Phản ứng tạo phức được ủ ở 4 ° C qua đêm trước khi phân tích bằng AGE và TEM.
AFM
Một giọt 20 μl dung dịch origami 10 nM RNA-6HB (MgCl2 nồng độ được điều chỉnh thành 12.5 mM) được lắng đọng trên đế mica mới cắt (Khoa học kính hiển vi điện tử) trong 1 phút, sau đó là ba bước rửa với 100 μl nước khử ion được làm mờ ngay lập tức. Mẫu được làm khô dưới dòng nitơ ổn định và chụp ảnh ngay sau khi chuẩn bị mẫu. Hình ảnh AFM được thu được trong không khí bằng cách sử dụng ScanAsyst ở Chế độ không khí cùng với đầu dò ScanAsyst-Air (Bruker) trên Biểu tượng thứ nguyên AFM (Bruker). Quá trình xử lý hình ảnh được thực hiện trong NanoScope Phân tích v.1.90 (Bruker).
TEM
Các mẫu origami DNA đơn giản (4 nM) đã được chuẩn bị bằng cách ủ một giọt 3 μl trong 3 phút trên plasma đã được làm sạch (đèn flash plasma oxy 20 giây, Gatan Solarus) Lưới đồng phủ carbon Formvar (FCF400Cu, Electron Microscopy Sciences), được sau đó thấm qua giấy lọc và nhuộm âm tính. Đối với các mẫu phức hợp CCMV-CP (origami DNA 4 nM), một giọt 3 μl được lắng đọng trên lưới trong 1.5 phút. Sau khi thấm qua giấy lọc, lưới được ngâm trong một giọt dung dịch đệm tạo phức 10 μl (3.25 mM HEPES-NaOH, 25 mM Tris–HCl, 150 mM NaCl, 0.5 mM DTT) trong 5 giây. Đối với các mẫu có nồng độ DNA origami 2 nM (ví dụ: tạo phức với SV40, MPyV) và đối với các mẫu chứa RNA-6HB (nồng độ origami 7.5 nM), kích thước giọt được tăng lên 5 μl và thời gian ủ kéo dài đến 5 phút . Nhuộm tiêu cực65 được thực hiện bằng cách lần đầu tiên nhúng lưới vào một giọt 5 μl dung dịch uranyl formate 2% (w/v) (bổ sung NaOH 25 mM để điều chỉnh pH), ngay lập tức bị xóa đi. Tiếp theo bước này là ngâm trong giọt 20 μl, được ủ trên lưới trong 45 giây. Sau bước làm mờ cuối cùng, các mẫu được để khô ít nhất 20 phút trước khi thực hiện chụp ảnh trên kính hiển vi FEI Tecnai 12 Bio-Twin ở điện áp gia tốc 120 V.
Cryo-EM
Các mẫu cho cryo-EM được chuẩn bị bằng thiết bị thủy tinh hóa (Vitrobot, Thermo Fisher Scientific). Nồng độ origami trong các mẫu được tạo phức là 90 nM đối với 6HB-2k, 84 nM đối với 24HB-2.5k, 18 nM đối với 6HB-10k và 21 nM đối với 24HB-10k, dẫn đến tổng nồng độ CP là 180 μM và 210 μM đối với các mẫu phức hợp. mẫu 6HB và 24HB tương ứng. Một phần 3 μl của mẫu origami phức tạp được đặt trên lưới được làm sạch bằng plasma (50 giây, dụng cụ Harrick Plasma PDC-002-EC) (đồng 200 lưới R1.2 / 1.3, Quantifoil). Sau 1 phút ủ, chất lỏng dư được thấm trong 10 giây ở độ ẩm tương đối 100% và 6 ° C, sau đó nhúng lưới vào ethane lỏng. Các lưới được lưu trữ trong nitơ lỏng. Dữ liệu được thu thập ở nhiệt độ nitơ lỏng trong kính hiển vi điện tử truyền qua Talos Arctica (Thermo Fisher Khoa học) hoạt động ở 200 kV, sử dụng máy dò điện tử trực tiếp Falcon III (Thermo Fisher Khoa học). Độ phóng đại 150,000× đã được sử dụng, dẫn đến kích thước pixel được hiệu chỉnh là 0.96 Å. Các tham số thu thập dữ liệu được liệt kê trong Bảng bổ sung 4 (Ghi chú bổ sung 24).
Tái thiết hạt đơn
Dữ liệu Cryo-EM được xử lý bằng CryoSPARC 3.3.2 (Công nghệ sinh học Structura) trừ khi có quy định khác. Các tham số hàm truyền tương phản được ước tính bằng CTFFIND4 (ref. 66). Các phân đoạn dọc theo sợi được xác định bằng chức năng Filament Tracer. Các tham số đối xứng xoắn ốc được ước tính ban đầu từ mức trung bình của lớp 2D bằng cách sử dụng Helix Indexer dựa trên Python67. Cấu trúc và các tham số đối xứng xoắn ốc được tinh chỉnh bằng cách sử dụng chức năng Helix Refine và sàng lọc không đồng nhất trên các đoạn xoắn ốc được điều chỉnh chuyển động. Để xác định các tham số đối xứng xoắn ốc của lớp ngoài 6HB-10k, lần chạy phân loại 2D thứ hai được thực hiện sau khi trừ đi phần đóng góp của lớp bên trong bằng hàm Trừ hạt. Helix Refine được chạy trên tập hợp con các hạt có lớp thứ hai rõ ràng, sử dụng các tham số đối xứng đã xác định làm ước tính ban đầu. Việc tái thiết đã được mài giũa bằng cách áp dụng một giải pháp đặc biệt B-hệ số −300 Å2. Việc tái tạo được tính trung bình trong không gian thực bằng cách áp đặt các tham số đối xứng xoắn ốc ở phần trung tâm, có trật tự nhất của bản đồ (50% thể tích) trong Bsoft68.
Để mô hình hóa cấu trúc của capsomer, monome CP (PDB: 1cwp) đã được lắp vào bản tái cấu trúc 6HB-2k ở sáu vị trí của hexamer dưới dạng vật thể cứng trong UCSF ChimeraX 1.3 (ref. 69). Mô hình nguyên tử đã được tinh chỉnh theo mật độ bằng cách sử dụng ISOLDE 1.3 (ref. 70) và Phenix 1.19 (ref. 71). Để tạo ra các biểu diễn nguyên tử của các sợi, các bản sao đối xứng của hexamer đã được tạo trong ChimeraX. Để hình dung vị trí của các hexamer CP và pentamer trong nắp, các nắp của dây tóc 6HB-2k đã được chọn thủ công trong ảnh vi mô. Cấu trúc nắp đã được tinh chỉnh bằng cách sử dụng chức năng Helix Refine bỏ qua tính đối xứng, vì điều này cho phép hạn chế góc nghiêng của nắp gần với các góc nhìn từ bên. Việc tái tạo nắp đã được lọc theo độ phân giải cục bộ bằng Bộ lọc cục bộ. Mô hình nguyên tử hexamer và cấu trúc pentamer đã được xác định trước đó (được trích từ PDB: 1cwp sau khi áp dụng tính đối xứng 1.3 mặt) được gắn dưới dạng vật thể cứng trong ChimeraX XNUMX. Các tham số xử lý dữ liệu được đưa ra trong Bảng bổ sung 4. Các tham số sàng lọc và xác nhận mô hình được hiển thị trong Bảng bổ sung 5.
SAXS
Các mẫu cho SAXS được chuẩn bị ở nồng độ origami là 165 nM (6HB, tương ứng với nồng độ CP đã tháo rời là 330 μM) và 180 nM (24HB, tương ứng với nồng độ CP đã tháo rời là 450 μM) và được niêm phong trong đường kính 1.5 mm mao mạch thủy tinh. Các phép đo được thực hiện bằng thiết bị Xenocs Xeuss 3.0C được trang bị nguồn lấy nét đồng GeniX 3D (bước sóng λ = 1.542 Å) và máy dò pixel lai EIGER2 R 1M ở khoảng cách máy dò mẫu-máy dò là 1,100 mm. Việc thu thập dữ liệu được thực hiện trong 3 × 3 giờ mỗi mẫu. Để có được dữ liệu SAXS 1D, dữ liệu tán xạ 2D được lấy trung bình theo phương vị. Độ lớn của vectơ tán xạ q được đưa ra bởi (q,=,4uppi sin theta /lambda) với 2θ là góc tán xạ. Xử lý dữ liệu bao gồm tính trung bình dữ liệu 2D ba lần của mỗi mẫu, phép trừ nền khỏi bộ đệm tạo phức (3.25 mM HEPES-NaOH, 25 mM Tris–HCl, 150 mM NaCl, 0.5 mM DTT) và một hệ số dạng được gắn vào một hình trụ ( 6HB, 24HB), hình cầu (T = 3 tổ hợp CP 6 mặt) và một hình trụ vỏ lõi (2HB-24k, 2.5HB-XNUMXk) bằng phần mềm SasView. Mô hình Debye–Anderson–Brumberger đã được thêm vào để làm nền.
- Phân phối nội dung và PR được hỗ trợ bởi SEO. Được khuếch đại ngay hôm nay.
- PlatoData.Network Vertical Generative Ai. Trao quyền cho chính mình. Truy cập Tại đây.
- PlatoAiStream. Thông minh Web3. Kiến thức khuếch đại. Truy cập Tại đây.
- Trung tâmESG. Ô tô / Xe điện, Than đá, công nghệ sạch, Năng lượng, Môi trường Hệ mặt trời, Quản lý chất thải. Truy cập Tại đây.
- BlockOffsets. Hiện đại hóa quyền sở hữu bù đắp môi trường. Truy cập Tại đây.
- nguồn: https://www.nature.com/articles/s41565-023-01443-x
- : có
- :là
- ][P
- 1
- 1: Tỷ lệ 1
- 1.3
- 10
- 100
- 11
- 116
- 12
- 14
- 15%
- 16
- 180
- 19
- 1M
- 2%
- 20
- 200
- 2011
- 2014
- 2015
- 2018
- 2019
- 2021
- 2022
- 2023
- 23
- 24
- 25
- 27
- 2D
- 30
- 31
- 32
- 3d
- 40
- 46
- 50
- 500
- 60
- 65
- 66
- 67
- 7
- 70
- 75
- 8
- 80
- 84
- 9
- 90
- a
- ở trên
- tăng tốc
- Tài khoản
- chính xác
- mua lại
- mua lại
- Ad
- thích nghi
- thêm
- Ngoài ra
- thêm vào
- Ngoài ra
- Điều chỉnh
- Điều chỉnh
- Sau
- chống lại
- tuổi
- Đại lý
- KHÔNG KHÍ
- AL
- cho phép
- dọc theo
- an
- phân tích
- Neo
- và
- Nộp đơn
- tiếp cận
- LÀ
- xung quanh
- AS
- lắp ráp
- hợp ngữ
- At
- trung bình
- xa
- lý lịch
- dựa
- BE
- được
- trước
- được
- giữa
- ràng buộc
- công nghệ sinh học
- cơ quan
- cả hai
- BP
- một thời gian ngắn
- đệm
- Xây dựng
- by
- CAN
- mũ lưỡi trai
- mũ
- Tế bào
- di động
- trung tâm
- Kênh
- sự lựa chọn
- tốt nghiệp lớp XNUMX
- phân loại
- trong sáng
- Nhấp chuột
- Đóng
- bộ sưu tập
- cạnh tranh
- tập trung
- điều kiện
- chứa
- tiếp tục
- Ngược lại
- đóng góp
- kiểm soát
- bản sao
- Copper
- Tương ứng
- tạo
- tạo ra
- dữ liệu
- xử lý dữ liệu
- xác định
- giao hàng
- mật độ
- Tùy
- ký gửi
- mô tả
- thiết kế
- mong muốn
- Xác định
- xác định
- phát triển
- thiết bị
- Lọc máu
- khác nhau
- kích thước
- trực tiếp
- khoảng cách
- dna
- xuống
- khô
- suốt trong
- năng động
- e
- E&T
- mỗi
- ed
- giáo dục
- hiệu lực
- cuối
- Kỹ Sư
- đảm bảo
- Môi trường
- như nhau
- đã trang bị
- ước tính
- dự toán
- Ether (ETH)
- ví dụ
- dư thừa
- Sàn giao dịch
- trao đổi
- biểu hiện
- tuyệt chủng
- yếu tố
- chim ưng
- NHANH
- này
- lọc
- bộ lọc
- cuối cùng
- tìm kiếm
- Tên
- Đèn flash
- sau
- Trong
- hình thức
- hình thành
- 4
- từ
- chức năng
- Hơn nữa
- được
- ly
- dần dần
- lưới
- Tăng trưởng
- hướng dẫn
- có
- tại đây
- Cao
- Tuy nhiên
- HTTPS
- Hỗn hợp
- i
- ICE
- ICON
- iii
- hình ảnh
- hình ảnh
- Hình ảnh
- ngay
- đắm mình
- ngâm
- áp đặt
- in
- bao gồm
- tăng
- ủ
- SỰ CỐ
- người lập chỉ mục
- ban đầu
- ban đầu
- cụ
- tích hợp
- tương tác
- Giao thức
- trong
- Ionic
- bị cô lập
- IT
- ITS
- KDA
- lớp
- ít nhất
- trái
- ánh sáng
- LINK
- Chất lỏng
- Liệt kê
- tải
- địa phương
- chính
- thủ công
- bản đồ
- Maps
- vật liệu
- đo
- đo
- đo lường
- mắt lưới
- phương pháp
- Mica
- Kính hiển vi
- Kính hiển vi
- phút
- hỗn hợp
- hỗn hợp
- di động
- Chế độ
- kiểu mẫu
- mô hình hóa
- mô-đun
- MOL
- phân tử
- giám sát
- hầu hết
- mRNA
- nano
- công nghệ nano
- Thiên nhiên
- tiêu cực
- được
- of
- on
- vận hành
- tối ưu hóa
- nếu không thì
- Kết quả
- qua đêm
- Ôxy
- Giấy
- thông số
- một phần
- hạt
- PBS
- PCR
- mỗi
- thực hiện
- Thể chất
- đã chọn
- Pitch
- điểm ảnh
- đặt
- Plasma
- nền tảng
- plato
- Thông tin dữ liệu Plato
- PlatoDữ liệu
- lao dốc
- vị trí
- chuẩn bị
- chuẩn bị
- trình bày
- trước đây
- mồi
- QUY TRÌNH
- thủ tục
- xử lý
- xử lý
- chương trình
- bảo vệ
- Protein
- Protein
- đã mua
- chất lượng
- khác nhau,
- tỉ lệ
- đạt
- đạt
- phản ứng
- thực
- thực tế
- đỏ
- lọc
- tinh chế
- về
- tương đối
- lặp đi lặp lại
- Báo cáo
- cần phải
- nhà nghiên cứu
- Độ phân giải
- tương ứng
- kết quả
- Kết quả
- cứng nhắc
- RNA
- Phòng
- chạy
- s
- muối
- SCI
- KHOA HỌC
- khoa học
- Thứ hai
- xem
- phân đoạn
- thay đổi
- ngắn
- cho thấy
- thể hiện
- bên
- Tương tự
- website
- Six
- Kích thước máy
- nhỏ hơn
- natri
- Phần mềm
- giải pháp
- Giải pháp
- nguồn
- Không gian
- chia
- quy định
- vững chắc
- Bước
- Các bước
- cổ phần
- là gắn
- lưu trữ
- Sợi
- dòng
- sức mạnh
- cấu trúc
- nghiên cứu
- Học tập
- Sau đó
- thành công
- hệ thống
- bàn
- talos
- Công nghệ
- việc này
- Sản phẩm
- cung cấp their dịch
- sau đó
- theta
- điều này
- số ba
- Thông qua
- thời gian
- thời gian
- đến
- bên nhau
- công cụ
- Tổng số:
- rút ra
- chuyển
- chuyển
- điều trị
- XOAY
- hai
- Dưới
- US
- sử dụng
- đã sử dụng
- người sử dang
- Giao diện người dùng
- sử dụng
- Vaccine
- HIỆU LỰC
- xác nhận
- linh hoạt
- Lượt xem
- Virus
- hình dung
- điện áp
- khối lượng
- khối lượng
- W
- là
- rửa
- Nước
- trọng lượng
- là
- cái nào
- trắng
- với
- ở trong
- không có
- X
- sản lượng
- zephyrnet